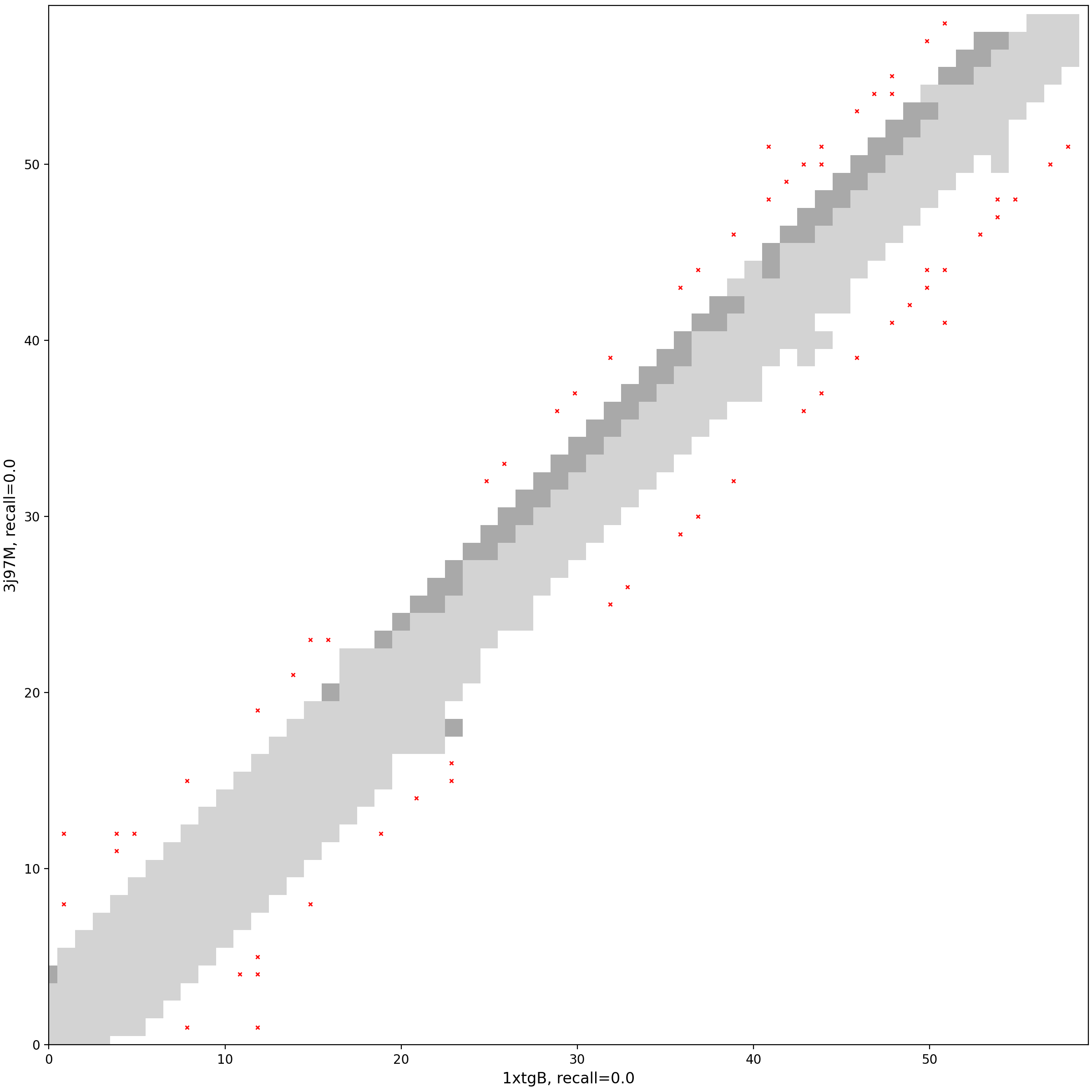
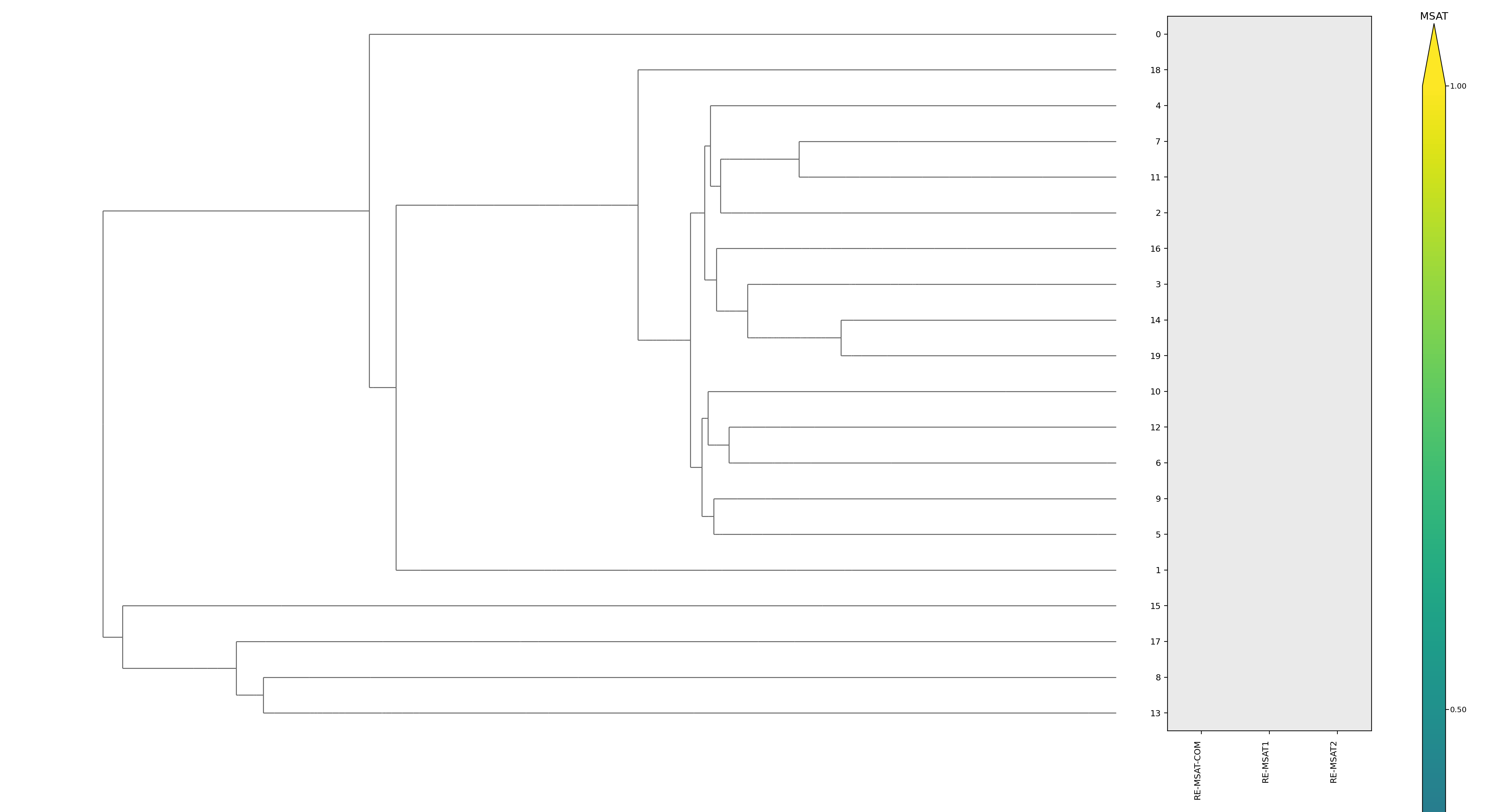
| cluster | n | neff | AF2_TM1 | AF2_TM2 | AF3_TM1 | AF3_TM2 | RE-MSAT-COM | RE-MSAT1 | RE-MSAT2 | ESM_SEQIDS | ESM_TM1_LIST | ESM_TM2_LIST |
|---|
| Deep | - | - | 0.35 | 0.48 | 0.35 | 0.47 | 0.0 | 0.0 | 0.53 | - | - | - |
| 000 | - | - | 0.35 | 0.43 | 0.34 | 0.43 | - | - | 0.0 | 003; 003; 008; 008; 004; 004; 007; 007; 001; 009 | 0.13; 0.13; 0.12; 0.12; 0.09; 0.09; 0.08; 0.08; 0.07; 0.07 | 0.09; 0.09; 0.08; 0.07; 0.07; 0.07; 0.09; 0.09; 0.04; 0.04 |
| 001 | - | - | 0.36 | 0.46 | 0.36 | 0.48 | 0.0 | 0.0 | 0.0 | 010; 010; 007; 007; 005; 005; 001; 001; 002; 002 | 0.15; 0.15; 0.14; 0.14; 0.14; 0.14; 0.13; 0.13; 0.12; 0.12 | 0.07; 0.07; 0.06; 0.06; 0.08; 0.08; 0.08; 0.08; 0.08; 0.08 |
| 002 | - | - | 0.34 | 0.43 | 0.34 | 0.42 | - | - | 0.0 | 005; 005; 004; 004; 007; 008; 008; 007; 003; 003 | 0.15; 0.15; 0.13; 0.12; 0.12; 0.12; 0.12; 0.12; 0.08; 0.08 | 0.08; 0.08; 0.08; 0.08; 0.07; 0.07; 0.08; 0.07; 0.09; 0.09 |
| 003 | - | - | 0.35 | 0.42 | 0.35 | 0.43 | - | - | 0.0 | 004; 004; 005; 006; 006; 005; 007; 007; 008; 008 | 0.14; 0.14; 0.13; 0.13; 0.13; 0.13; 0.09; 0.09; 0.08; 0.08 | 0.08; 0.08; 0.08; 0.08; 0.08; 0.08; 0.08; 0.09; 0.10; 0.09 |
| 004 | - | - | 0.35 | 0.42 | 0.34 | 0.42 | - | - | 0.0 | 004; 006; 006; 004; 007; 007; 001; 003; 009; 008 | 0.15; 0.15; 0.15; 0.15; 0.09; 0.09; 0.07; 0.07; 0.07; 0.07 | 0.08; 0.07; 0.07; 0.08; 0.10; 0.10; 0.05; 0.09; 0.08; 0.10 |
| 005 | - | - | 0.35 | 0.43 | 0.34 | 0.42 | - | - | 0.0 | 008; 008; 007; 007; 001; 002; 009; 006; 005; 004 | 0.14; 0.14; 0.09; 0.09; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.07; 0.07; 0.09; 0.09; 0.04; 0.06; 0.04; 0.04; 0.10; 0.09 |
| 006 | - | - | 0.34 | 0.37 | 0.34 | 0.37 | - | - | 0.0 | 007; 007; 005; 005; 001; 002; 009; 008; 006; 004 | 0.09; 0.09; 0.08; 0.08; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.07; 0.08; 0.04; 0.04; 0.05; 0.05; 0.05; 0.06; 0.04; 0.05 |
| 007 | - | - | 0.35 | 0.42 | 0.35 | 0.42 | - | - | 0.0 | 009; 009; 004; 004; 006; 006; 001; 003; 008; 007 | 0.14; 0.14; 0.12; 0.12; 0.08; 0.08; 0.07; 0.07; 0.07; 0.07 | 0.07; 0.07; 0.07; 0.07; 0.04; 0.06; 0.05; 0.08; 0.04; 0.04 |
| 008 | - | - | 0.35 | 0.43 | 0.34 | 0.42 | - | - | 0.0 | 009; 009; 004; 008; 008; 004; 005; 005; 003; 003 | 0.15; 0.15; 0.14; 0.14; 0.14; 0.14; 0.11; 0.11; 0.09; 0.09 | 0.08; 0.08; 0.09; 0.07; 0.07; 0.09; 0.08; 0.08; 0.09; 0.10 |
| 009 | - | - | 0.34 | 0.39 | 0.33 | 0.37 | - | - | 0.0 | 006; 006; 009; 009; 008; 007; 008; 001; 003; 005 | 0.13; 0.13; 0.10; 0.10; 0.08; 0.08; 0.08; 0.07; 0.07; 0.07 | 0.07; 0.07; 0.05; 0.05; 0.08; 0.07; 0.08; 0.05; 0.04; 0.05 |
| 010 | - | - | 0.34 | 0.38 | 0.34 | 0.38 | - | - | 0.0 | 003; 003; 005; 005; 001; 002; 009; 008; 007; 006 | 0.09; 0.09; 0.08; 0.08; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.04; 0.04; 0.07; 0.07; 0.05; 0.04; 0.04; 0.04; 0.04; 0.04 |
| 011 | - | - | 0.35 | 0.43 | 0.35 | 0.43 | - | - | 0.0 | 003; 003; 005; 005; 004; 004; 001; 009; 008; 007 | 0.14; 0.14; 0.09; 0.09; 0.08; 0.08; 0.07; 0.07; 0.07; 0.07 | 0.09; 0.09; 0.09; 0.10; 0.07; 0.07; 0.05; 0.04; 0.04; 0.04 |
| 012 | - | - | 0.34 | 0.4 | 0.34 | 0.39 | - | - | 0.0 | 001; 002; 009; 008; 007; 006; 005; 004; 003; 002 | 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.04; 0.05; 0.05; 0.04; 0.04; 0.04; 0.05; 0.05; 0.05; 0.05 |
| 013 | - | - | 0.35 | 0.48 | 0.34 | 0.46 | 0.0 | 0.0 | 0.0 | 009; 009; 001; 001; 008; 008; 005; 006; 007; 004 | 0.15; 0.15; 0.13; 0.13; 0.12; 0.12; 0.07; 0.07; 0.07; 0.07 | 0.07; 0.07; 0.08; 0.08; 0.08; 0.08; 0.09; 0.05; 0.04; 0.10 |
| 014 | - | - | 0.35 | 0.43 | 0.34 | 0.43 | - | - | 0.0 | 003; 003; 006; 005; 005; 007; 007; 002; 002; 006 | 0.15; 0.15; 0.13; 0.12; 0.12; 0.12; 0.12; 0.12; 0.12; 0.11 | 0.08; 0.07; 0.07; 0.08; 0.09; 0.08; 0.08; 0.07; 0.07; 0.07 |
| 015 | - | - | 0.35 | 0.43 | 0.35 | 0.43 | - | - | 0.0 | 006; 004; 006; 004; 003; 002; 002; 003; 005; 007 | 0.15; 0.15; 0.15; 0.15; 0.13; 0.13; 0.13; 0.13; 0.08; 0.08 | 0.08; 0.07; 0.08; 0.07; 0.08; 0.07; 0.07; 0.08; 0.09; 0.09 |
| 016 | - | - | 0.35 | 0.43 | 0.34 | 0.42 | - | - | 0.0 | 004; 004; 010; 005; 006; 006; 010; 005; 003; 009 | 0.14; 0.14; 0.08; 0.08; 0.08; 0.08; 0.08; 0.08; 0.07; 0.07 | 0.07; 0.07; 0.06; 0.10; 0.09; 0.09; 0.07; 0.10; 0.03; 0.09 |
| 017 | - | - | 0.35 | 0.42 | 0.35 | 0.43 | - | - | 0.0 | 004; 004; 005; 005; 003; 003; 007; 007; 001; 009 | 0.15; 0.15; 0.13; 0.13; 0.12; 0.12; 0.12; 0.12; 0.07; 0.07 | 0.08; 0.08; 0.07; 0.07; 0.08; 0.08; 0.08; 0.08; 0.05; 0.05 |
| 018 | - | - | 0.35 | 0.42 | 0.35 | 0.42 | - | - | 0.0 | 001; 002; 009; 008; 007; 006; 005; 004; 003; 002 | 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.05; 0.03; 0.04; 0.04; 0.04; 0.04; 0.05; 0.04; 0.04; 0.03 |
| 019 | - | - | 0.34 | 0.42 | 0.34 | 0.42 | - | - | 0.0 | 009; 006; 006; 009; 001; 002; 008; 007; 005; 004 | 0.14; 0.14; 0.14; 0.14; 0.07; 0.07; 0.07; 0.07; 0.07; 0.07 | 0.08; 0.07; 0.07; 0.08; 0.05; 0.05; 0.09; 0.04; 0.09; 0.05 |